Towards Gene Expression Convolutions using Gene Interaction Graphs
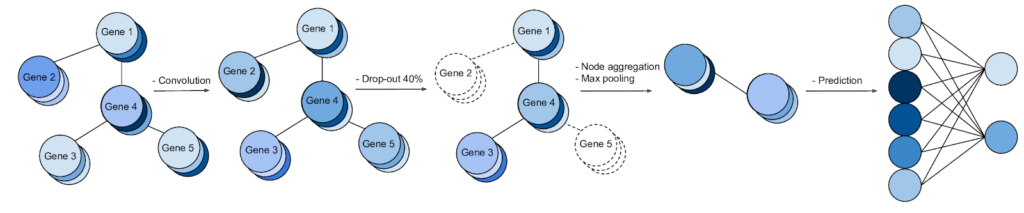
Nous discutons de la façon dont les graphes d’interaction gène-gène (même voie, protéine-protéine, co-expression ou association de texte de recherche) peuvent être utilisés pour imposer un biais à un modèle de réseau neuronal profond similaire au biais spatial imposé par les convolutions à une image. Nous trouvons que cette approche offre un avantage pour des tâches particulières dans un régime de données peu élevé, mais dépend beaucoup de la qualité du graphique utilisé. Plus d’informations: Paper Slides Code
Citation
Francis Dutil, Joseph Paul Cohen, Martin Weiss, Georgy Derevyanko, Yoshua Bengio. “Towards Gene Expression Convolutions Using Gene Interaction Graphs.” International Conference on Machine Learning (ICML) Workshop on Computational Biology (WCB), 2018, http://arxiv.org/abs/1806.06975
Reference
[arXiv:1806.06975] [ICML-WCB2017 Workshop on Computational Biology]